
- 首页
- >
- GENESEED
- >
9个常用circRNA研究数据库,助力你的研究!
为助力各位科研人从高通量数据中快速锁定 circRNA 研究靶点,本文整理了目前文献中常用的9个circRNA相关数据库(已核对至2026年最新可用网址),供各位科研工作者参考和收藏备用。
circRNA基础信息与表达分析数据库
circBase
网址:http://www.circbase.org
特点与适用场景:提供circRNA ID、基因组定位及序列等基础信息,是领域内引用率最高的经典数据库。主要用于初步确认候选靶点是否已被既往文献报道。需注意其数据更新频率较低。
circBank
网址:http://www.circbank.cn/
特点与适用场景:涵盖人、小鼠等多种模式生物的综合性数据库。提供 circRNA 标准化命名体系、成熟 circRNA 序列、不同组织或发育阶段的表达谱、miRNA 结合位点以及蛋白翻译潜能预测等全方位信息。
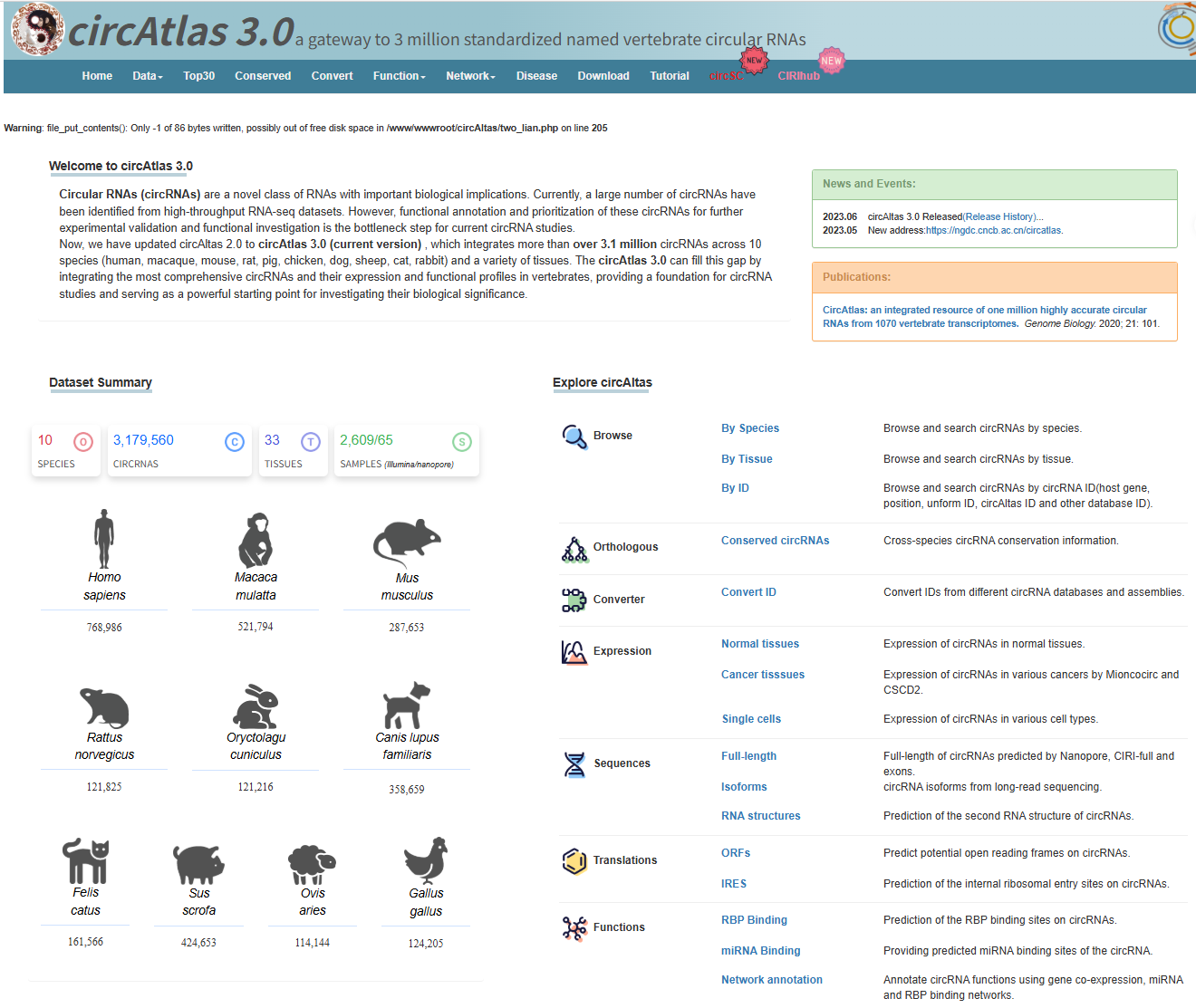
circAtlas 3.0
网址:https://ngdc.cncb.ac.cn/circatlas/
特点与适用场景:
数据规模与来源:3.0版本整合了超过300万条 circRNA数据,并补充了Nanopore长读长测序数据。
标准化命名:采用统一的标准化命名系统,解决了跨数据库间ID比对不一致的问题,提高了数据检索的效率。
多维度分析:支持特定组织及单细胞水平的表达谱查询,适用于筛选高丰度靶点以及开展跨物种的保守性研究。
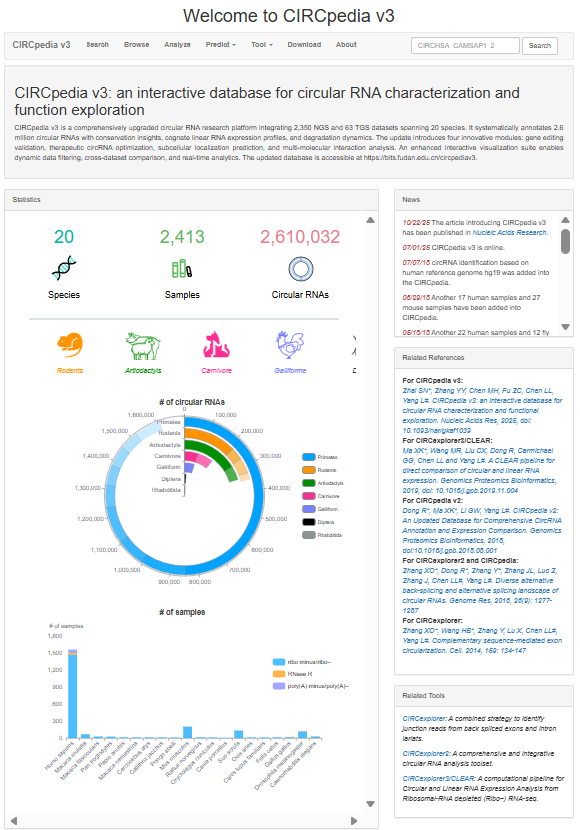
CIRCpedia v3
网址:https://bits.fudan.edu.cn/circpediav3/
特点与适用场景:
数据覆盖与更新:v3版本扩展至20个物种,整合2000余个测序样本并注释约260万个circRNA(原中科院旧网址已停用)。
环/线表达定量对比:支持利用统一量化参数(FPB)对比circRNA与同源线性mRNA的表达差异,辅助高丰度差异靶点的筛选。
功能预测与实验设计:内置了引物设计、siRNA/sgRNA筛选、亚细胞定位、m6A修饰及翻译潜能预测等模块,可直接服务于后续的干扰验证及分子机制研究。
circRNA互作与网络构建数据库
CircInteractome
网址:https://circinteractome.nia.nih.gov
特点与适用场景:提供人源 circRNA 与 miRNA 及 RBP(RNA 结合蛋白)结合位点的在线预测。内置跨剪接位点(BSJ)的发散引物设计工具,可辅助 ceRNA 机制研究中的结合位点筛选及后续的 PCR 定量验证。

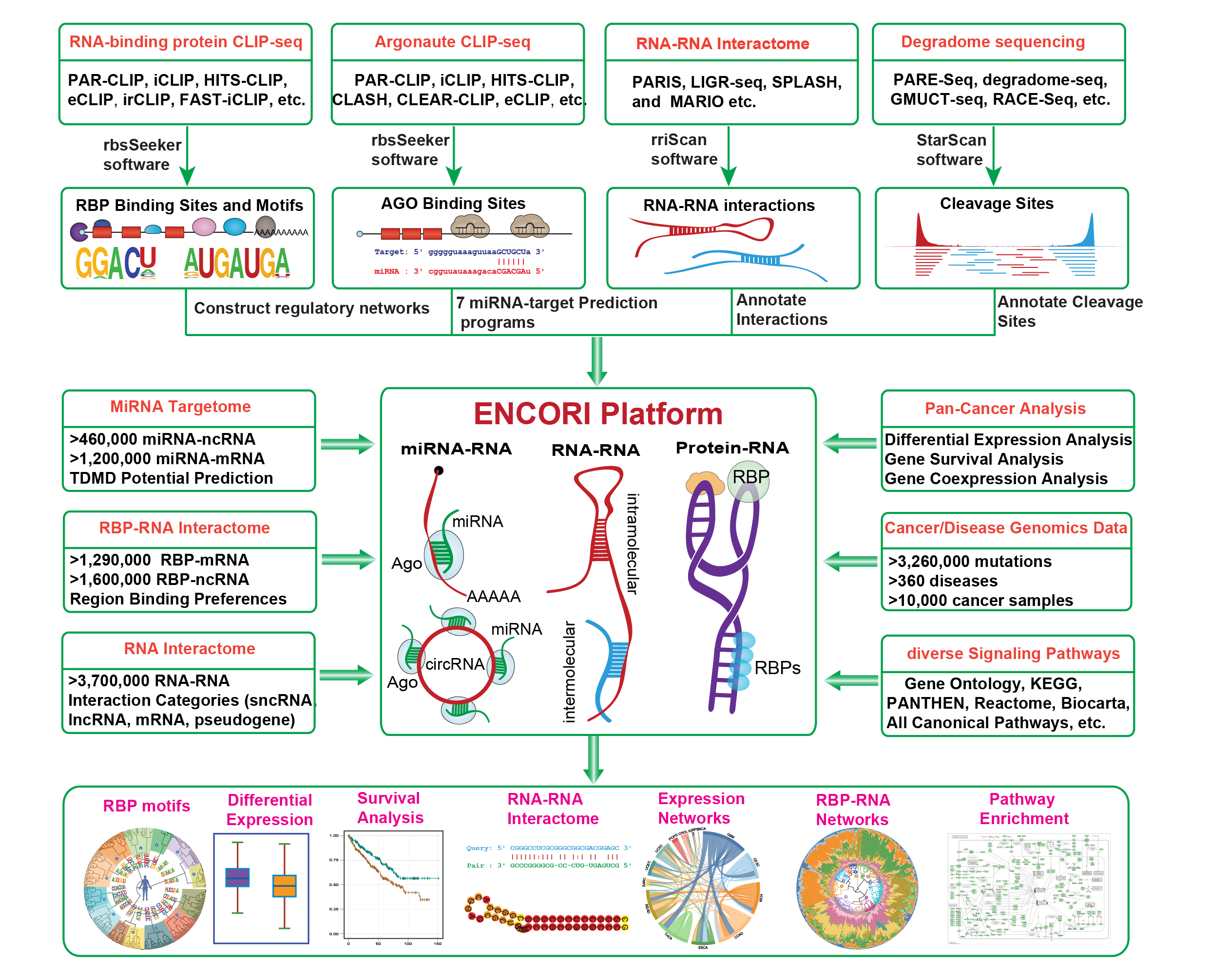
starBase/ENCORI
网址:https://starbase.sysu.edu.cn
特点与适用场景:基于CLIP-seq等多组学测序数据提供circRNA-miRNA互作及ceRNA网络分析。整合了多类肿瘤临床样本数据,支持泛癌水平的生存分析与相关性研究。

疾病、标志物与肿瘤相关circRNA数据库
circRNADisease 2.0
网址:https://cgga.org.cn/circRNADisease/
特点与适用场景:收录经文献报道和实验验证的 circRNA 与疾病关联信息。涵盖多种临床疾病靶点,适合在研究初期针对特定疾病进行已知靶点的查漏补缺。

exoRBase 3.0(外泌体与标志物专属)
网址:http://www.exorbase.org/
特点与适用场景:专注于人类血液等体液外泌体中的RNA表达图谱,整合了正常人与各类疾病患者的测序数据。适用于筛选和开发体液circRNA无创诊断标志物。

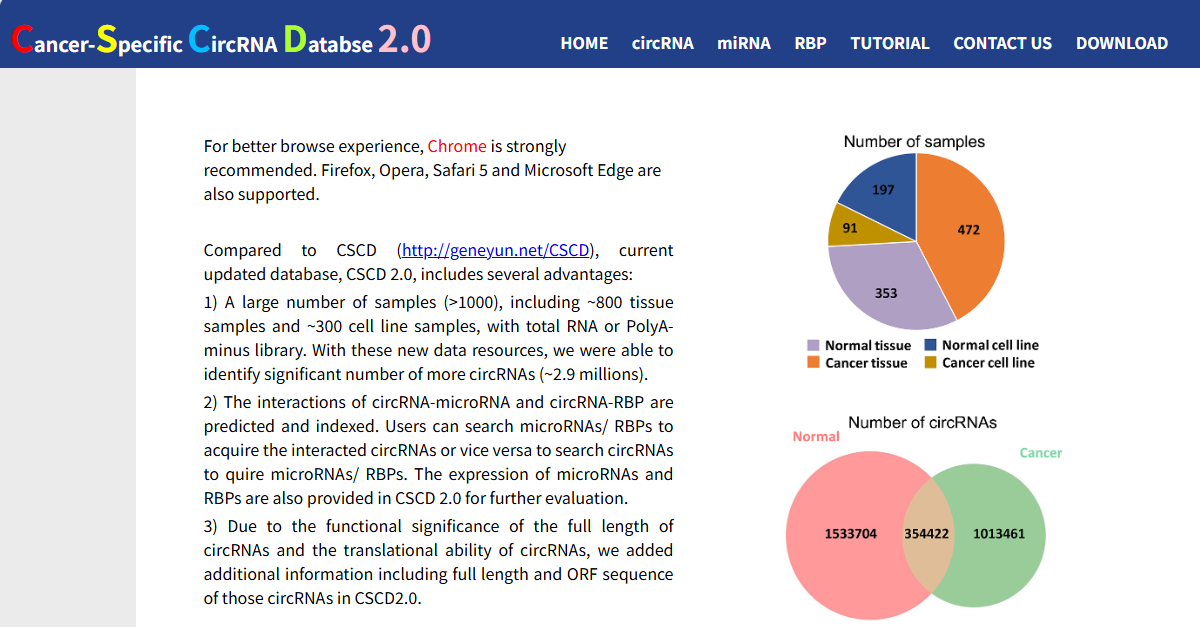
CSCD 2.0
网址:http://geneyun.net/CSCD2
特点与适用场景:专注于肿瘤特异性circRNA,收录逾100万个癌症相关靶点。提供miRNA/RBP结合位点及开放阅读框(ORF)预测,可用于癌症机制研究中的靶点精确筛选与翻译潜能分析。
在实际操作中,您最常用的 circRNA 数据库是哪一个?或者有哪些‘冷门好用’的工具推荐?欢迎在留言区分享,我们一起探讨。

 购物车
购物车




 广州市黄埔区开源大道11号科技企业加速器A区6栋2楼
广州市黄埔区开源大道11号科技企业加速器A区6栋2楼


 geneseed@geneseed.com.cn
geneseed@geneseed.com.cn